本文
【生命科学コース】雑穀のきた道ー論文を発表(福永教授)
福永教授の論文が国際誌Genes and Genetic Systemsに早期公開(Advance Online Publication)されました。
Kenji Fukunaga, Akira Abe, Keisuke Tanaka, Masaya Tsuji, Makoto Kawase
Phylogenetic and population genomic analysis of foxtail millet (Setaria italica)
landraces via ddRAD-seq, with emphasis on Japanese germplasm
(アワ在来品種の系統・集団ゲノム解析ー特に日本品種に注目して)
Genes and Genetic Systems https://doi.org/10.1266/ggs.26-00012
【解説】
作物の歴史を探ることは我々人類がどのように広がってどのように生きてきたのかという問いとも関わってきます。福永研究室では、雑穀の一つであるアワについて研究をしています。アワは黄河文明の主食であり、日本を含むアジアやヨーロッパで古くから重要な作物でした(日本では五穀の一つとされてきましたし、現在でも新嘗祭ではイネとともに献上される穀物です)。
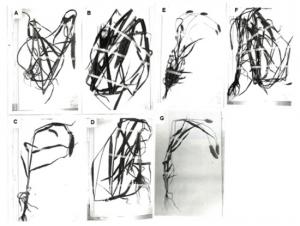
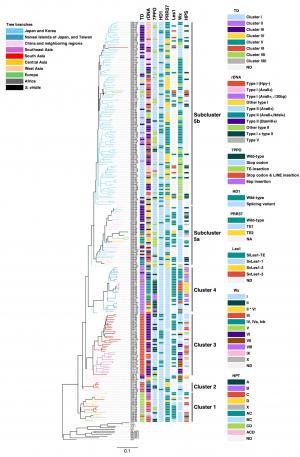
本研究では、世界各地のアワの在来品種(近代以前の品種)240品種と野生種であるエノコログサ11系統について、次世代シークエンサー(NGS)*を用いて解析方法の一つであるddRAD-seq** という方法を用いて、多型解析を行い、得られたデータを基に系統樹を作成するとともに集団構造解析を行い、世界中の品種がどのような類縁関係にあるのか?日本の品種はどこの品種と系統的に近いのか?品種が分かれてから交雑などが起こっているのか?を明らかにするとともに、これまで福永研などで調査してきた、胚乳デンプンのモチ・ウルチに関わる遺伝子、ポリフェノールの酸化に関わる遺伝子、出穂期に関わる遺伝子、脱粒性に関わる遺伝子などの遺伝子型とも比較を行いました。
結果として、
1) アワはエノコログサから一元的に生じた可能性が高い。
2) アワの品種は地理的な品種分化をとげており地理的なグループにわかれる。
3) 考古学的に中国起源が有力であるが、エノコログサに近いのはユーラシア西部の品種であった。栽培化後に品種の移動などがあったなど考えるべきなのか、検証を要する。
4) 用いた材料は在来品種であるが、フランスの品種やインドの1品種など比較的最近に東アジアの品種との交雑があったことがうかがえる。これはここの遺伝子の結果などとも一致している。
5) 個々の遺伝子の遺伝子型と系統樹を比較すると、栽培化初期に分化したであろう遺伝子(出穂期に関するHD1遺伝子やポリフェノール酸化酵素(PPO)遺伝子)や、地域品種に分化する過程や分化したあとで分化した遺伝子(出穂期に関するPRR37遺伝子やWx遺伝子)というように遺伝子によって分化の時期が異なることが示唆された。後者は地理的に広がる適応や人為選抜によって分化したものであろうと考えられる。
6) 日本の品種は、韓国と系統的にかなり近く元は中国の品種から分化した九州以北グループと台湾と近縁な沖縄(南西諸島)グループに明瞭に分かれる。ごく一部中間的なものもあるがこのふたつの分化は明瞭である。
本研究は、県立広島大学の福永研究室と岩手生物工学研究センター、東京農業大学との共同研究として行われました。また、研究成果は部分的に科研費(20K06098, 23K05279)の助成を受けています。ddRAD-seqの解析は東京農業大学「生物資源ゲノム解析拠点事業」で行われました。
福永教授が全体のデザインと論文の執筆、院生(当時)の辻君が一部材料の栽培やDNA抽出、岩手生物工学研究センターの阿部研究員(現・研究部長)がインフォマティクスの解析と論文執筆、NGSの解析を東京農大(現・東京情報大)の田中研究員、全体の助言やディスカッションを東京農大・河瀬教授(当時)が担当しました。
また、個々の遺伝子の解析は、これまでに福永研究室に所属した学生の皆さんの協力によるものです。既に論文として発表済ですが、福永研究室のこれまでの仕事の積み上げによって今回のような論文での考察ができました。
我々の文明に礎になるのは、1万年から数千年前の農耕の開始ですが、福永研究室では、作物がどのように野生種からうまれたのか?起源地から広がる過程で環境への適応や人への嗜好性に応じてどのような遺伝子に選抜がかかったのかについて、遺伝学の研究を行っています。過去数千年、われわれはどのようにして環境に対応してきたのか?という問いは、先の見えない環境変動にどのように立ち向かっているのかにもつながってきます。
福永研の日々の様子はインスタグラムでも発信しています。
* 次世代シークエンサー(NGS) : 生物の遺伝情報を高速で解読する機械で、技術的な革新を引き起こしています。ここ20年ぐらいに普及しておりさまざまな生物でゲノム情報(全遺伝子)を解読できるようになっています。それまでの方法はサンガー法によるものでした(高校の教科書など参照)。
** ddRAD-seq: 個体間や品種間を調べるのに、全ゲノムを解読して比較するのも手ですが、お金がかかるので、ゲノムの一部をランダムに取り出すさまざまな方法が考案されています。そのうちのひとつで、2種類の制限酵素を用いたのちのNGSで多くの多型を検出する方法です。他に同様な目的のための方法として、RAD-seqやGras-Di, MIG-seqやdpMIG-seqなどがあります。


最近の関連記事
【生命科学コース】新連載!教員ロングインタビュー1・福永教授
【生命環境学科生命科学コース】卒業生の声-福永研の4人の卒業生(前編)
【生命環境学科生命科学コース】卒業生の声-福永研の4人の卒業生(後編)
【生命環境学科生命科学コース】卒業生の声-研究にたずさわる3人の同級生 (山谷さん)
【生命環境学科生命科学コース】卒業生の声-福永研の卒業生(2)
 大学概要
大学概要
 学部・大学院・専攻科
学部・大学院・専攻科
 学生生活・就職支援
学生生活・就職支援
 研究・地域連携・国際交流
研究・地域連携・国際交流
 入試情報
入試情報